La réparation de l'ADN
Adapté par Jean-Yves Dupont
A partir d'un article de Beth A. Montelone
Division of Biology, Kansas State University
Avec l'autorisation de l'auteur
LES SYSTEMES DE REPARATION DE L'ADN
Les dommages à l'ADN intervenant spontanément et résultant d'agents de l'environnement existant en permanence, la plupart des organisme possèdent des capacités à réparer leur ADN.
L'ADN est la seule macromolécules à être réparée par les cellules.
Les mécanismes sont de trois types :
- la restauration de la zone endommagée : c'est le plus simple. Un action enzymatique restaure la structure sans casser le squelette
- la suppression de la zone endommagée : les bases ou le groupe de nucléotides incorrects sont remplacés.
- la tolérance de la zone endommagée : il n'y a pas de réparation ; le dommage est accepté.
La restauration de la zone endommagée
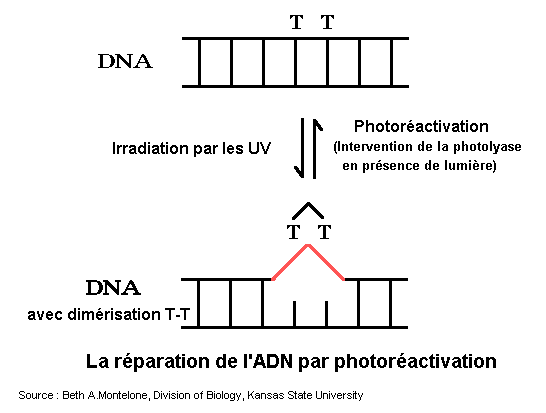
1 - La photoréactivation
|
Il est la fois le plus simple et sans doute le plus ancien des systèmes de réparation. Une simple enzyme peut dissocier la dimérisation (en cassant les liaisons covalentes) en présence de lumière. L'enzyme est une photoligase : elle existe chez de nombreuses bactéries, les eucaryotes inférieurs, les insectes et les plantes. Elle semble absente chez les Mammifères bien que le gène soit présent mais il code pour une autre protéine qui a un rôle accessoire dans un autre mode de réparation. |
 |
2 - La réparation des ruptures sur un seul brin
Les rayons X et quelques produits chimiques comme les peroxydes peuvent causer des ruptures dans le squelette de l'ADN.
Les ruptures sur un seul brin sont rapidement réparées par une ligase. Les microbes mutants n'ayant pas cette ligase ont tendance à avoir des taux de recombinaisons élevés puisque les extrémités de l'ADN sont très recombinantes. On connaît un cas chez l'Humain (46BR) avec des mutations sur les deux gènes codant pour les ligases I de l'ADN : sa croissance est ralentie ; il est immuno-déficient, a une sensibilité accrue aux UV et décède précocement d'un lymphome. Les fibroblastes de 46BR sont très sensibles aux agents mutagènes. Le bloom syndrome (déficience héréditaire rare) est également en rapport avec une déficience de la ligase de l'ADN (bien que la protéine mise en cause soit une ADN hélicase). Les patients ont de fort taux d'aberrations chromosomiques et de nombreuses mutations spontanées.
La suppression de la zone endommagée
1 - La réparation par excision de bases
La base inappropriée est détachée de sa liaison avec le sucre et remplacée. Ce sont des glycosylases qui rompent la liaison. Par exemple l'uracile-glycosylase sépare l'uracile de l'ADN. L'uracile n'est pas habituellement dans l'ADN, mais peut exister si la cytosine est déaminée (ce qui est potentiellement mutagène). L'enzyme reconnaît l'uracile et coupe la liaison glycosyl avec le déoxyribose. La base est alors excisée et une nouvelle base est insérée par la polymérase en utilisant le deuxième brin comme matrice. Les mutants qui ont une absence de l'uracile-glycosylase ont un taux élevé de mutations (la mutation C->U n'est pas réparée ce qui aboutit à des transitions) et il y a une hypersensibilité à l'acide nitreux (ce qui entraîne des mutations C->U par déamination)
2 - La réparation des mauvais appariements
Ce processus intervient après la réplication de l'ADN à la manière d'un "correcteur orthographique". Il est réalisé par un groupe de protéines qui peuvent "scanner" l'ADN et détecter les paires de bases incorrectes ou mal appariées. Le nucléotide incorrect est supprimé et l'ADN -polymérase opère un deuxième passage pour rétablir la séquence convenable.
Des protéines réparatrices de mauvais appariements ont été récemment identifiées chez l'Homme. Elles sont très semblables à celles de l'Escherichia Coli et la levure ; des mutations ayant une incidence sur ces protéines affectent la lignée germinale et génèrent quelques cancers héréditaires (colon).
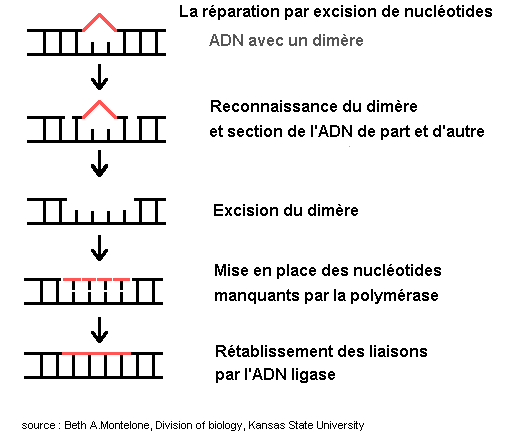
3 - La réparation par excision de nucléotides
Ce mécanisme intervient sur les dommages importants de l'ADN qui créent des blocages de la réplication et de la transcription (tels que les dimères induits par les UV et des produits chimiques).
Ainsi l'affection héréditaire Xeroderma pigmentosum caractérisée par une sensibilité accrue au soleil est responsable de l'apparition de cancers de la peau dans les zones exposées. Ils ont des gènes de réparation par excision déficients. Les organismes inférieurs présentant une sensibilité accrue aux UV ont un taux élevé de mutations : ils sont incapables de réparer les dimères de pyrimidine et font appel à des systèmes mutagènes ou recombinants.
La tolérance de la zone endommagée
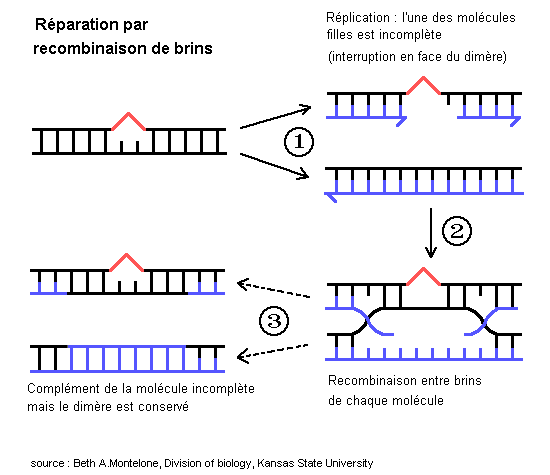
Tous les dommages de l'ADN ne peuvent être réparés immédiatement. Certains persistent. Si un œil de réplication contient des altérations (par exemple un dimère de pyrimidine), il y a normalement blocage de la réplication.
Cependant, chez les Eucaryotes, la réplication peut être initiée à de nombreux endroits. Elle peut donc reprendre au delà du dimère, laissant un secteur de la molécule non répliqué. Ceci peut avoir des conséquences importantes en cas de division cellulaire. Toutefois, il y a un moyen de réparation par recombinaison avec l'autre chromatide ou la chromatide sœur,ce qui aboutit à deux molécules sœur intactes, l'une d'elle contenant encore le dimère.
1 - La réparation par recombinaison entre molécules-filles
Ce mécanisme induit une recombinaison pour résoudre une interruption sur l'une des molécule-fille et traiter une lésion non codante sur l'ADN. Ce mode est en général précis (bien que pouvant être à l'origine de doubles allèles récessifs altérés). Il requiert une chromatide-sœur ou homologue.
Les produits des gènes de susceptibilité au cancer du poumon (gène BRCA1 et BRCA2) peuvent être concernés par ce type de réparation (homologues des gènes RAD51 et RAD52 de la levure).
Un autre type de réparation par recombinaison (utilisé pour réparer les extrémités cassées de l'ADN) est la réaction d'union d'extrêmités non homologues. Ce système est aussi employé par les Lymphocytes B et T pour les réarrangements géniques. Les protéines KU70, KU80 et la proténe-kinase ADN-dépendante sont requises. Les lignées cellulaires déficientes au niveau de ces gènes sont sensibles aux radiations ionisantes et déficients dans le réarrangement pour les cellules immunitaires.
2 - La réparation mutagène
Un scénario alternatif au blocage de la réplication par un dimère est d'insérer un nucléotide en face du dimère pour poursuivre la réplication (scénario "mute" ou "meurt").
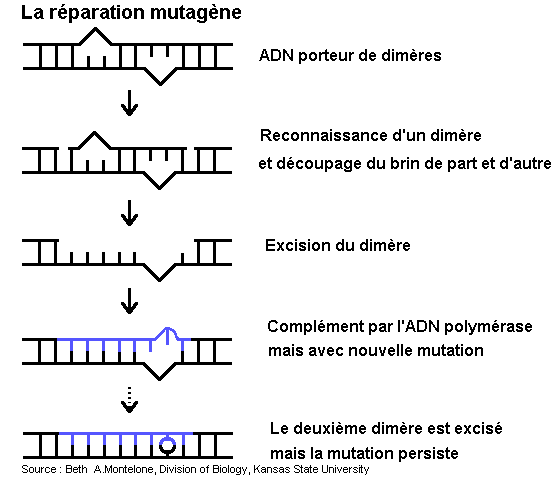
Ce mécanisme est connu chez les bactéries et intervient probablement chez les Eucaryotes.