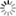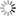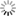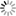Suivi des variants SARS-CoV-2
Structure du Spike de Sars-CoV-2
D'après : Cryo-EM structure of the 2019-nCoV spike in the prefusion conformation
Daniel Wrapp et ali.
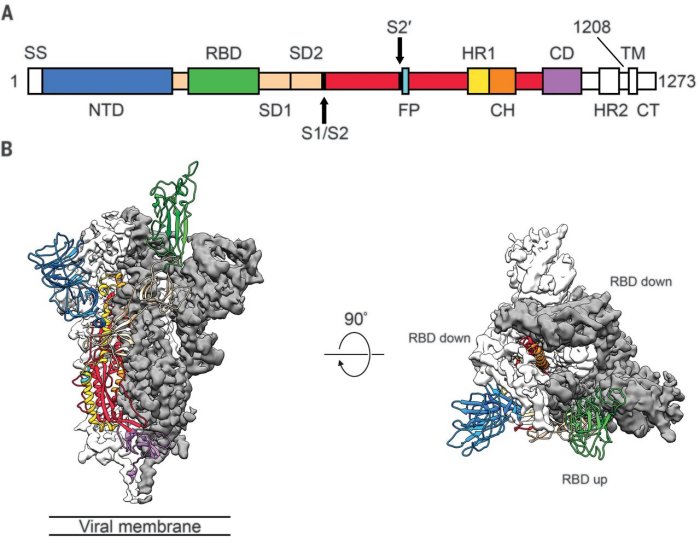
Fig. 1 Structure of 2019-nCoV S in the prefusion conformation.
(A) Schematic of 2019-nCoV S primary structure colored by domain. Domains that were excluded from the ectodomain expression construct or could not be visualized in the final map are colored white. SS, signal sequence; S2′, S2′ protease cleavage site; FP, fusion peptide; HR1, heptad repeat 1; CH, central helix; CD, connector domain; HR2, heptad repeat 2; TM, transmembrane domain; CT, cytoplasmic tail. Arrows denote protease cleavage sites. (B) Side and top views of the prefusion structure of the 2019-nCoV S protein with a single RBD in the up conformation. The two RBD down protomers are shown as cryo-EM density in either white or gray and the RBD up protomer is shown in ribbons colored corresponding to the schematic in (A).
Séquences pour Anagène
 |
Résultats des comparaisons
Comparaison des molécules S (Spike. 1273 aa). Matrice obtenue avec Géniegen 2.
Nombre de mutations dans la protéine S (Référence Wuhan).
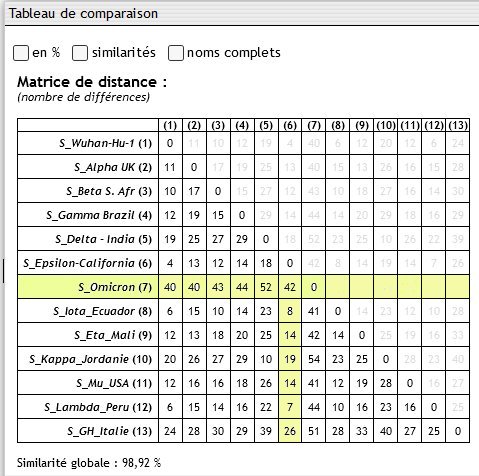
Comparaison des RBD (Receptor binding domain. 319-541 . 223 aa). Matrice obtenue avec Géniegen 2.
Nombre de mutations dans le RBD de la protéine S (Référence Wuhan).
Comparaison des RBM (Receptor binding motif. 437-507. 71 aa). Matrice obtenue avec Géniegen 2.

Nombre de mutations dans le RBM de la protéine S (Référence Wuhan).
Localisation des mutations dans le RBM de la protéine Spike
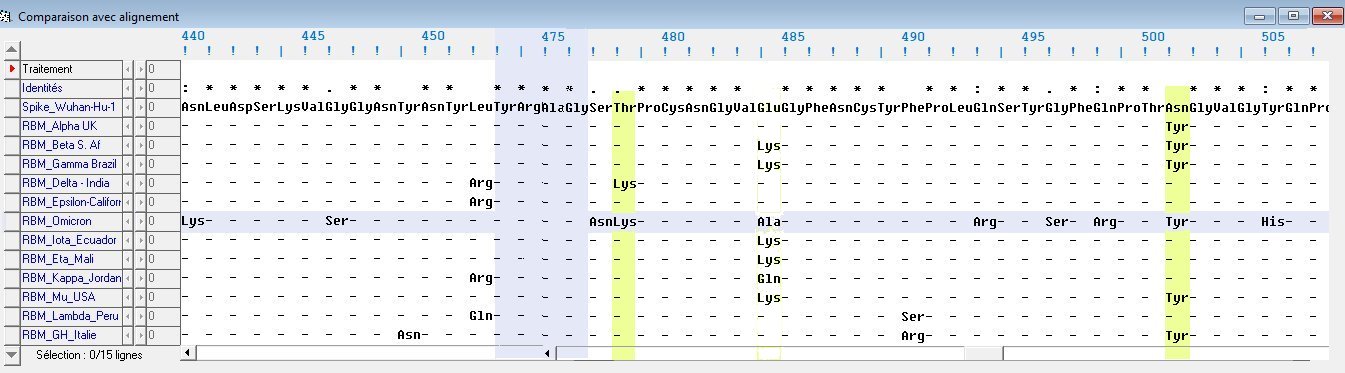
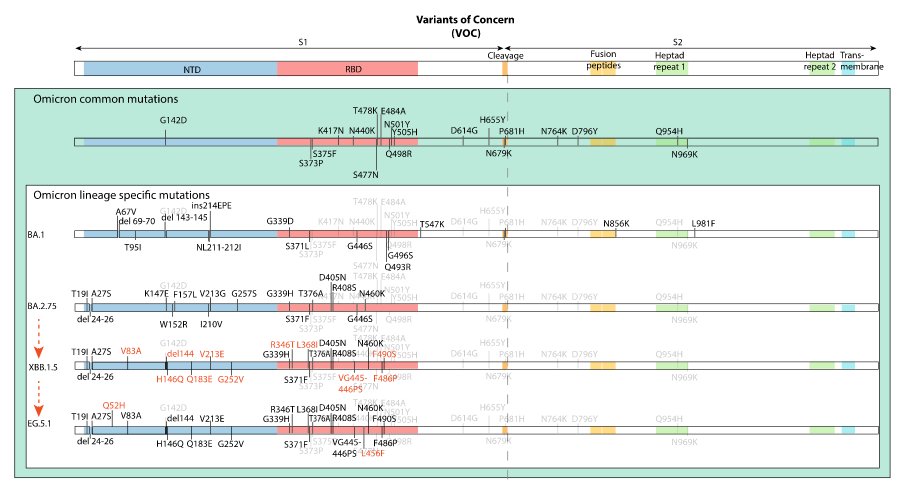
Colonnes en jaune : mutations dans Omicron communes avec d'autres variants.
Schématisation de Spike avec localisation des mutations dans différents variants
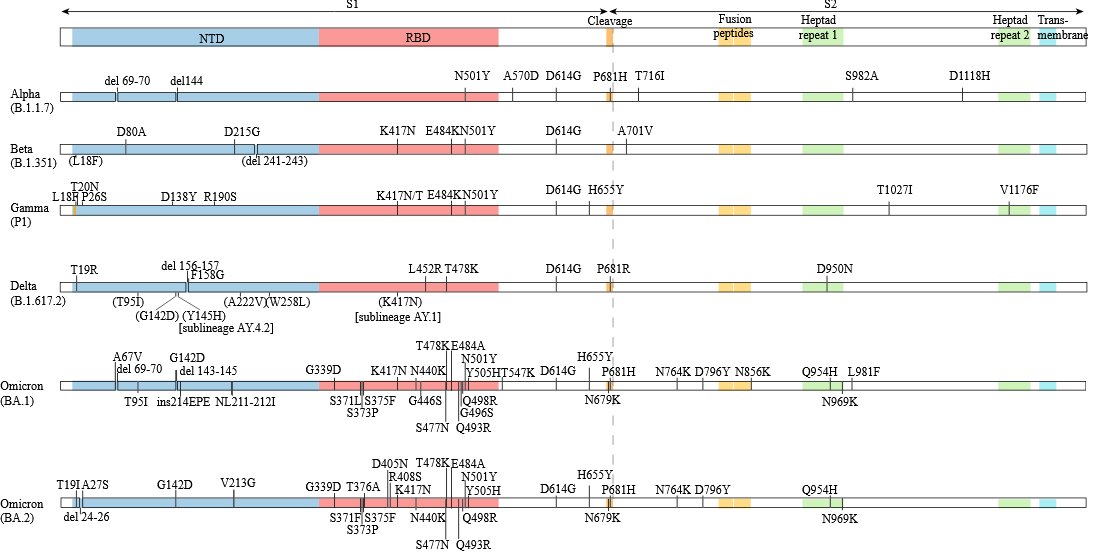
Variants Omicron d'intérêt (02/05/2024)
Séquences de la protéine S des variants (au 19/08/2023). Pour Anagène
Positions en interaction avec ACE2
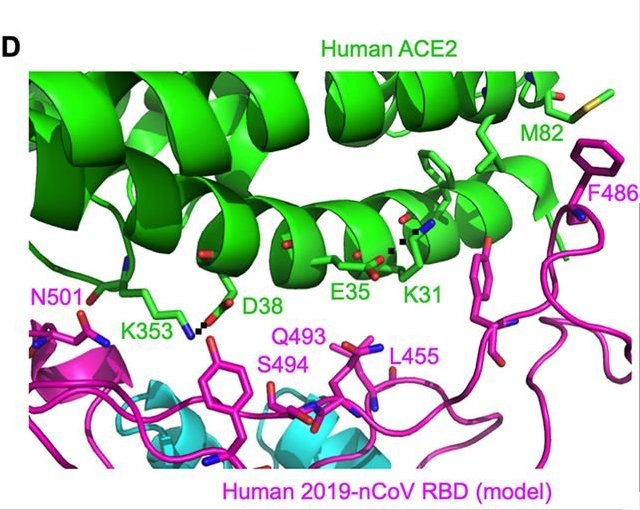
Image extraite de l'article : Receptor Recognition by the Novel Coronavirus from Wuhan: an Analysis Based on Decade-Long Structural Studies of SARS Coronavirus. Yushun Wan et al. J Virol. 2020 Mar 17.
Suivi des variants SUR :
| Gisaid | Viral Zone | ||
| Nextstrain | Site OMS |