L'action des enzymes de restriction
Par jfmadre
—
Dernière modification
04/03/2025 10:52
Lorsque l'on étudie des séquences d'ADN, on peut simuler l'action d'une ou plusieurs enzymes de restriction. Le logiciel permet aussi de rechercher une enzyme qui coupe différemment 2 allèles.
Cette recherche sera traitée sur l'exemple de la G6PD (glucose-6-phosphate déshydrogénase). Lorsque le gène est muté, cela provoque une destruction des globules rouges (hémolyse). Il s'agit de rechercher des enzymes de restriction qui coupent différemment l'allèle normal (G6PDB) et l'allèle muté (G6PD_morb).
- Comparaison des deux séquences (en mode d'affichage Comparaison)
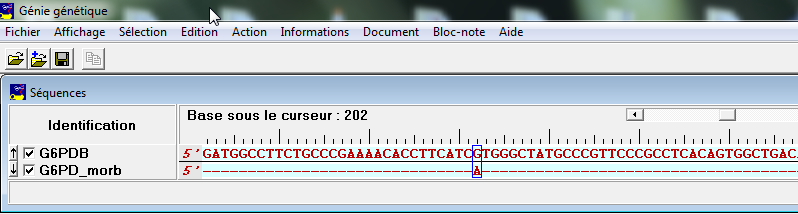
- Recherche d'une enzyme qui reconnaît une zone de mutation (ici la base 202)
Utiliser le menu Action/Enzyme de restriction, la fenêtre suivante s'affiche :
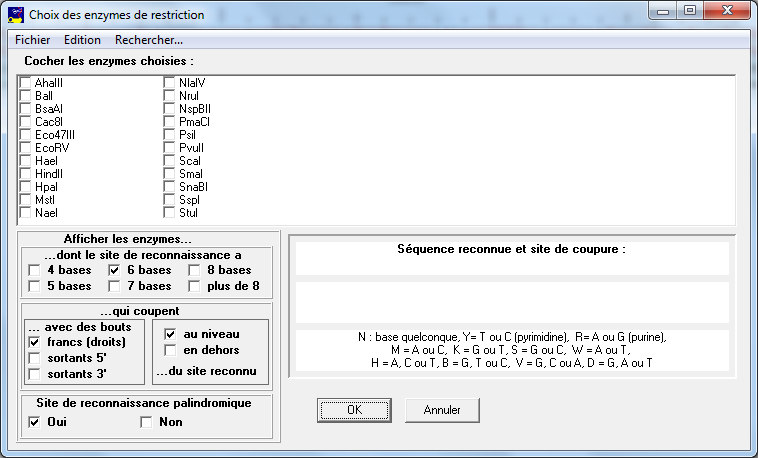
Pour qu'il y ait un choix plus large d'enzymes, cocher tous les types d'enzymes du cadre en bas à gauche de la fenêtre.
Puis cliquer sur le menu Rechercher... pour faire afficher la fenêtre de recherche :
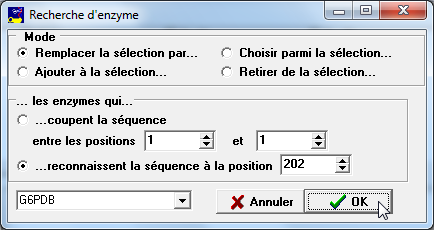
Ici on recherchera les enzymes qui reconnaissent la séquence à la position 202 (qui est différente pour les deux allèles).
Remarque : en choisissant ensuite un autre mode, on pourrait combiner successivement plusieurs critères (par exemple tenir compte des autres sites de mutation avec le mode "ajouter à la sélection"...
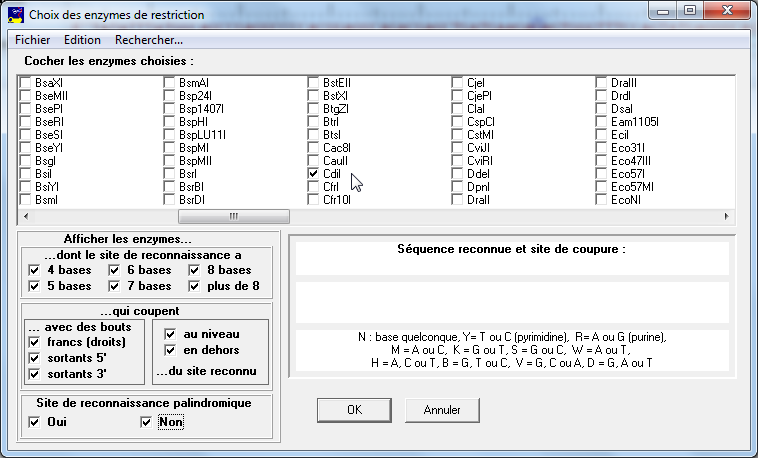
Avec le seul critère choisi ici, une seule enzyme (CdiI) a été sélectionnée.
En cliquant sur OK, on obtient Le mode de coupure de la première séquence. - Comparaison des coupures
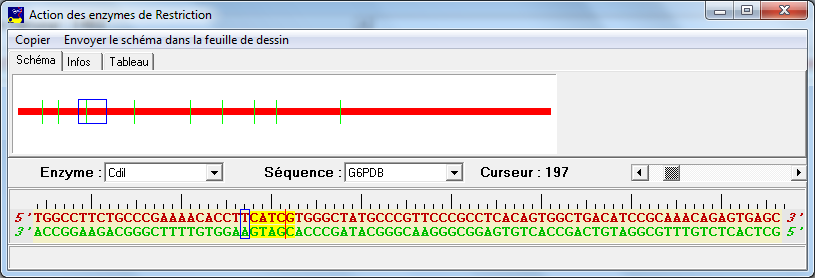
En se déplaçant dans la séquence au voisinage de la base 202, on observe une coupure de l'allèle normal par l'enzyme. La séquence de l'allèle muté étant différente à cet endroit, on n'observe pas de coupure :
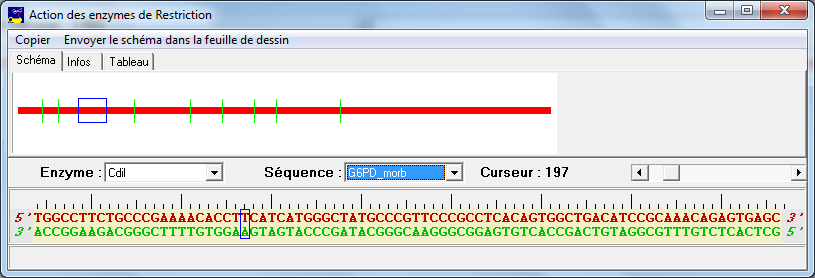
- L'électrophorèse de l'allèle normal coupé par l'enzyme CdiI donnera 10 fragments et seulement 9 pour l'allèle muté. Cela permet de les différencier.
- Les infos et le tableau résument les résultats.
