Les outils de traitement des séquences
Le menu Action offre différentes possibilités :
- Alignement (ou alignement choisi)
- Transcription (ou Transcription inverse)
- Traduction
- Chaine complémentaire
- Mutation (simulation)
- Recherche
- Enzyme de restriction
Transcription ou transcription inverse
Dans les deux cas une petite fenêtre apparaît avec la liste des séquences qui se prêtent à l'opération (ADN pour la transcription ou ARN pour la transcription inverse). Voici un exemple qui concerne la transcription :
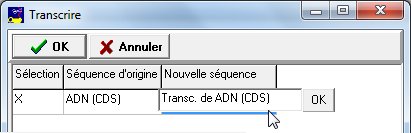 Cliquer sur le nom proposé (Nouvelle séquence) pour pouvoir le modifier. Valider le nouveau nom par le petit bouton OK
Cliquer sur le nom proposé (Nouvelle séquence) pour pouvoir le modifier. Valider le nouveau nom par le petit bouton OK  puis valider l'opération avec le bouton
puis valider l'opération avec le bouton  de la fenêtre. La séquence transcrite apparaîtra comme une nouvelle séquence, indépendante de la séquence d'origine. Elle sera enregistrée par exemple si on choisit de faire un enregistrement des séquences sélectionnées.
de la fenêtre. La séquence transcrite apparaîtra comme une nouvelle séquence, indépendante de la séquence d'origine. Elle sera enregistrée par exemple si on choisit de faire un enregistrement des séquences sélectionnées.
L'opération est donc différente de celle obtenue avec les choix d'affichage. Dans ce dernier cas, la séquence transcrite reste dépendante de la séquence d'origine et possède la même référence (elle ne serait pas enregistrée en cas de sauvegarde sur un fichier).
Pour désélectionner une séquence à transcrire, cliquer sur la case X correspondante.
Traduction
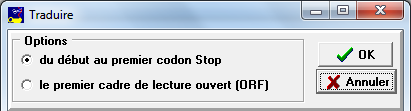
La fenêtre se présente de manière analogue à celle de la transcription avec ici toutes les séquences d'ADN et d'ARN. Il y a aussi le choix entre 2 modes de traduction :
|
Dans les deux cas, la traduction s'arrête au premier codon Stop. |
du début au premier codon Stop commence la traduction au début de la séquence même si ce n'est pas un codon initiateur le premier cadre de lecture ouvert, lui commence au premier codon initiateur (ATG ou AUG) |
Ici encore ce sont de nouvelles séquences qui sont ainsi crées, ce qui est différent des traductions obtenues avec le menu Affichage.
Chaîne complémentaire
La fenêtre est encore analogue à celle des actions précédentes :
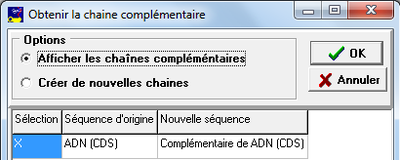 |
Le premier choix est un simple effet d'affichage, comme celui obtenu avec le menu affichage. Le deuxième choix crée une nouvelle séquence qui sera affichée dans le sens 5'3', classique pour l'ADN. Sur l'affichage elle ne sera pas en relation avec la séquence d'origine. |
Simulation de mutations
Le menu Action/Mutation/Simulation ouvre une fenêtre où l'on peut définir la mutation à opérer.
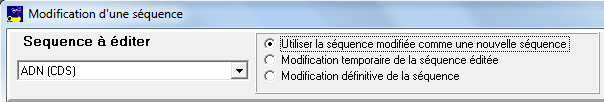
il faut d'abord choisir la séquence dans la boîte à onglet et ce que deviendra la mutation : nouvelle séquence, modification temporaire qui pourra être supprimée par le menu Action/Mutation/Annuler tout (ou Annuler la dernière) ou modification définitive de la séquence d'origine.
On peut alors choisir le type de mutation et, si on crée une nouvelle séquence le nom de cette séquence.
- Substitution
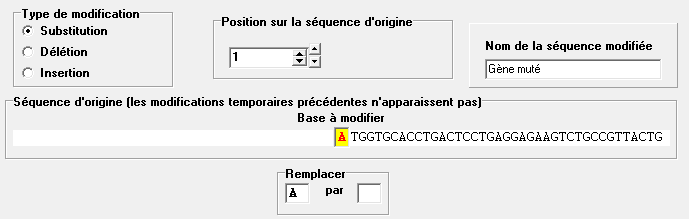
Choisir la position sur la séquence et taper, en bas le symbole de la base qui remplacera celle d'origine.
- Délétion
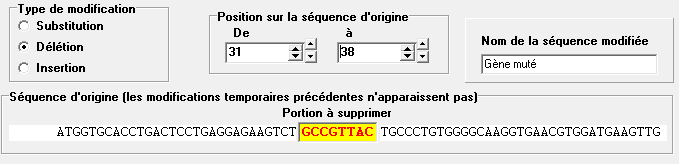
Choisir la zone à supprimer.
- Insertion
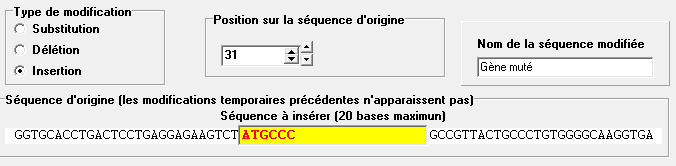
Taper les symboles des bases à ajouter.
Dans tous les cas, Valider en cliquant sur le bouton OK.
Recherche
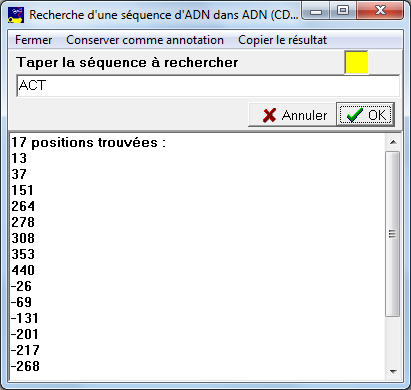
Le menu Action/Recherche permet de rechercher une portion de séquence dans la première séquence affichée.
|
|
Lorsque l'on a tapé la séquence à rechercher et cliqué sur le bouton OK, les positions de la séquence sont affichées. (Étendre la fenêtre vers le bas ou utiliser l'ascenseur si nécessaire). Les valeur négatives correspondent à la chaîne complémentaire si la séquence recherchée s'y trouve dans le sens normal (5'3') |