Réplication et expression de l’information génétique au cours du cycle infectieux du coronavirus
Réplication et expression de l’information génétique au cours du cycle infectieux du coronavirus |
Jean-Claude Hervé, Naoum Salamé
Documents
- The genomic organization and virus structure of SARS-CoV-2
- Structure du Sars-CoV- 1 (nature reviews microbiology 2003)
- Structure détaillée du génome de Sars-CoV-2. D'après un article du New York Times
- Possible life cycle of Sars-Cov-2
- Life cycle of a coronavirus (extrait de Learning from the past)
Séquences
Lien vers GenBank
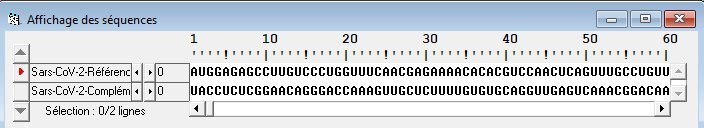
Deux brins complémentaires de la séquence Sars-CoV-2 en ARN.
-
Sars-CoV-2-Référence-ADN-ARN.edi
Séquence de référence de Sars-CoV-2 en ADN et en ARN - Spike-CoV-2-ARN-Protéine.edi
La séquence en ARN de Spike-CoV-2 mise en parallèle avec sa traduction et la protéine de GenBank.
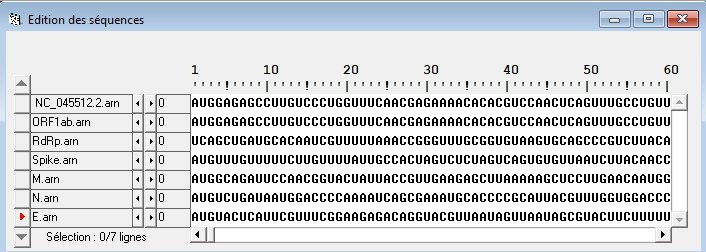
Séquences nucléiques ORF1ab, RdRp, 3CLpro, PLpro, Spike, M, N, E en ADN et en ARN.
Séquences protéiques de ORF1ab, RdRp, 3CLpro, PLpro, Spike, M, N et E.
La réplication de l’ADN, l’expression de l’information génétique, les enzymes sont au programme de spécialité de première en SVT. Les données sur les coronavirus et plus précisément sur le Sars-CoV-2 offrent l’occasion de réinvestir ces notions à partir d’une activité reposant sur la comparaison des mécanismes de réplication du génome viral avec ceux en œuvre chez les eucaryotes dont la connaissance est donc un prérequis.
Avant de commencer cette étude, il est souhaitable de faire un point élémentaire sur la structure des coronavirus et donc du Sars-CoV-2 responsable de la pandémie actuelle.
1 . Structure des coronavirus
On connait actuellement 7 coronavirus humains : HKU1 ; NLC3, OL43, 229E, MERS-Cov, Sars-CoV-1 et Sars-Cov-2. Les 4 premiers sont à l’origine de troubles respiratoires modestes alors que les trois derniers (apparus respectivement en 2012, 2002 et 2019) peuvent entraîner des détresses respiratoires graves.
Les virions de ces coronavirus, grossièrement sphériques, ont leur surface hérissée de spicules qui forment une couronne, d’où leur nom.
Les figures ci-dessous illustrent de façon schématique les structures du Sars-CoV-1 et du Sars-CoV-2.
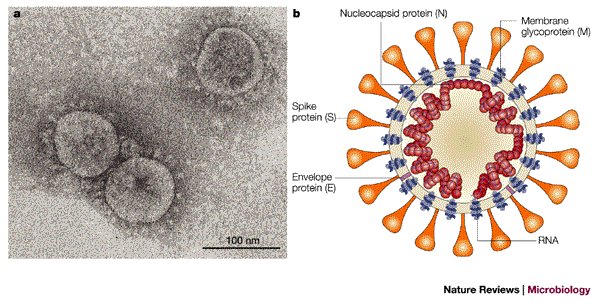
- Structure du Sars-CoV-1. Image extraite de l'article SARS — beginning to understand a new virus. Konrad Stadler et al. Nature Reviews Microbiology volume 1, pages209–218 (2003)

- Structure du Sars-CoV-2. Image extraite de l'article : Potential Therapeutic Targets and Promising Drugs for Combating SARS-CoV-2. Zhou, Hong et al. May 6, 2020
La structure de ces virus est très semblable. Ce sont des virus enveloppés, l’enveloppe étant une bicouche lipidique d’origine cellulaire (membrane des cellules parasitées).
Dans cette enveloppe sont insérées 4 types de protéines structurales :
- Les protéines S (Spike) qui assurent la liaison avec des récepteurs des cellules à infecter. Pour les Sars-CoV-1 et Sars-CoV-2, le récepteur présent sur les cellules épithéliales des bronches et des alvéoles pulmonaires est ACE2.
- Les protéines M qui possèdent trois domaines transmembranaires et qui donnent sa forme au virus.
- Les protéines E qui servent à l’assemblage et à la libération des virions hors de la cellule infectée.
- Les protéines N qui s’associent au génome viral et forment un complexe ribonucléique.
2 . Le génome viral
Il est constitué par un brin d’ARN de près de 30kbases (29903 pour Sars-CoV-2. Voir la séquence de référence. Lien vers GenBank).
Le document ci-dessus en donne une représentation très simplifiée à partir des protéines codées par le génome. La séquence amont nommée ORF1ab représente plus des deux tiers du génome et code pour 16 protéines dont plusieurs sont des enzymes qui jouent un rôle essentiel dans la réplication et l’expression du génome. Les protéines structurales S, M, E et N associées à l’enveloppe du virion sont codées par des gènes situés vers l’extrémité 3’, de même que des protéines accessoires (3, 6, 7a, 7b ,8, 9b) dont les rôles ne sont pas bien élucidés.
Cette représentation suffit pour aborder les mécanismes de réplication et d’expression du génome des coronavirus Sars-CoV-1 et Sars-CoV-2. Le point important est que le génome du virus ne code pas uniquement des protéines structurales mais aussi des protéines non structurales, enzymatiques, dont le rôle est crucial dans la cellule infectée.
Une représentation plus complète du génome est disponible dans les documents complémentaires : Structure détaillée du génome de SARS-CoV-2. (Adaptation d'un article du New York Times).
La séquence de référence du virus SARS-CoV-2 présente l’intérêt de fournir les limites des différents gènes et de bien visualiser que ce génome viral est formé par une succession de gènes sans séquences non codantes entre eux.
3 . Le cycle viral
Il peut servir, en premier lieu, d’introduction à la recherche sur la comparaison de la réplication et de l’expression du génome du coronavirus et de celui des eucaryotes.
Les figures ci-dessous fournissent deux représentations schématiques du cycle viral.
- D’après : Learning from the past: possible urgent prevention and treatement options for severe acute respiratory infections caused by 2019-nCov. Jared R Morse et al. European chemical societies, ChemBioChem. 05 February 2020.
Cliquer sur l'image pour l'agrandir.
D'après : Potential Therapeutic Targets and Promising Drugs for Combating SARS-CoV-2. Zhou, Hong et al. May 6, 2020.
Cliquer sur l'image pour l'agrandir.
Sur les deux représentations, on voit un virion qui s’attache à une cellule cible par l’intermédiaire de ses protéines spike liées aux récepteurs ACE2. On visualise aussi les nombreux virions qui sont relachés par la cellule infectée. Puisque chaque virion produit contient un génome en ARN et des protéines structurales, cela signifie qu’au sein de la cellule il y a eu une réplication du génome viral et une production de protéines virales, ce qui implique l'expression du génome viral.
On peut alors dégager les grandes modalités de la réplication du génome et de son expression chez les eucaryotes pour voir si elles peuvent s’appliquer au virus.
- La réplication de chaque molécule du génome eucaryotique est semi conservative et repose sur une caractéristique essentielle : la complémentarité des deux brins d’ADN de la molécule.
- Puisque le génome viral est en ARN et monocaténaire, la réplication de ce génome est nécessairement différente. On peut imaginer des solutions possibles basées sur la notion de complémentarité.
L’ARN du génome viral ressemble à un ARN messager eucaryotique sauf qu’il ne code pas pour une protéine mais pour plusieurs. Joue-t-il le rôle d’un ARN messager chez le virus ? On peut le tester à partir de la séquence du gène codant pour la Spike et de celle de la protéine. Il suffit de traduire la séquence de ce gène et de comparer la séquence traduite à celle de la protéine issue de la banque (NCBI-GenBank) pour constater qu’elles sont identiques.

L’ARN viral peut être qualifié d’ARN messager. En réalité, en virologie on le qualifie d’ARN brin positif ce qui signifie seulement qu’il est traduit directement en protéines.
Comme le VIH et plus généralement le génome des rétrovirus, celui des coronavirus est en ARN. Cependant le cycle des coronavirus est bien différent de celui des rétrovirus. Il se déroule uniquement dans le cytoplasme de la cellule parasitée et jamais le génome n'est incorporé dans celui de la cellule.
Le génome des coronavirus ne possède pas de gène codant pour une transcriptase inverse catalysant la transcription de l'ARN en ADN. En revanche il code pour une ARN polymérase ARN dépendante (RdRp) qui, au sein du cytoplasme de la cellule, va assurer sa réplication.
Artificiellement, lors d'un test PCR, on convertit l'ARN viral prélevé en ADN pour amplifier les génomes recueillis chez une personne contaminée et les identifier.
Pour finir cette partie introductive, on peut s’interroger sur la raison qui conduit à exprimer dans les banques de données la séquence du coronavirus en ADN alors que jamais dans le cycle viral, il n’apparait (contrairement au rétrovirus) de phase en ADN. C’est une convention d’écriture. Pour toutes les molécules d’ADN on n’indique que la séquence d’un seul brin, celle du brin non transcrit qui est la même que celle de l’ARN messager sauf que les nucléotides à thymine remplacent ceux à uracile. Les logiciels traduisent aussi bien l’ADN que l’ARN messager. En conséquence, pour le génome du coronavirus on l’a exprimé en ADN car lorsqu’il est traduit par les logiciels il fournit la même séquence qu’avec l’ARN messager.
4 . Le premier évènement du cycle viral
L’objectif n’est pas d’étudier tous les aspects du cycle viral mais uniquement ceux qui sont en rapport avec l’expression et la réplication du génome. On peut donc passer au stade où le génome viral nu est libéré dans le cytoplasme de la cellule infectée.
Le premier cycle viral montre cet ARN avec des ribosomes. Ces ribosomes ne peuvent appartenir qu’à la cellule parasitée. Autrement dit, grâce à la machinerie cellulaire de traduction de la cellule, l’ARN viral comme un ARN messager, est traduit en protéines. Le code génétique est le même pour le virus et la cellule.
A vrai dire, tout le génome viral n’est pas traduit dans ce premier cycle ; seule l’est la région du segment ORF1ab. Celui-ci est traduit en une polyprotéine de 16 protéines. Le premier cycle viral souligne la présence dans cette polyprotéine de deux protéines 3Clpro et Plpro qui sont des protéases. Elles « coupent » les liaisons entre les protéines et libèrent dans le cytoplame cellulaire les protéines individuelles comme le visualisent les deux schémas du cycle. En particulier est libérée une enzyme appelée RdRp (faisant partie d’un complexe enzymatique appelé réplicase sur le deuxième schéma). Cette enzyme joue un rôle fondamental dans la poursuite du cycle.
Jusque là rien d’original dans le cycle viral puisque la traduction de l’ARN viral se fait comme celle d’un ARN messager en empruntant la machinerie cellulaire hôte.
5. La réplication du génome viral
Là on peut analyser une nouvelle molécule apparue dans la cellule infectée, appelée ARN brin négatif. La comparaison de cet ARN avec l’ARN viral montre que les deux brins sont complémentaires.
Le problème de la synthèse de ce brin complémentaire se pose alors. Le génome de la cellule infectée code pour une ADN polymérase et une ARN polymérase. Cette dernière catalyse la synthèse d’un ARNm à partir de la séquence d’un brin d’ADN. Comme toutes les enzymes, elle montre une spécificité de substrat et ne catalyse pas la synthèse d’un ARN à partir d’une séquence d’ARN préexistante. Mais parmi les protéines virales synthétisées lors de la traduction du génome viral, il y a un complexe enzymatique comprenant notamment une ARN polymérase ARN dépendante (RdRp). Cette enzyme virale catalyse la synthèse d’un brin d’ARN négatif qu’on qualifie parfois d’antigénome.
Ce dernier va alors servir de matrice pour la synthèse de brins complémentaires d’ARN c’est-à-dire de génomes viraux du coronavirus. Cette synthèse est permise grâce à l’enzyme RdRp.
La réplication du génome viral est différente de celle du génome des eucaryotes parce que le génome est en ARN et à un seul brin. Mais finalement on constate qu’elle repose sur une propriété commune qui est celle de la synthèse d’un brin complémentaire d’une séquence matrice initiale mais avec un système enzymatique différent.
6 . La synthèse des protéines structurales.
Le deuxième document sur le cycle viral indique que la réplicase et donc l’ARN polymérase ARN dépendante assure non seulement la réplication du génome viral à partir du brin négatif d’ARN mais aussi la production de séquences virales qualifiées de subgénomiques. Chaque séquence d’ARN subgénomique code pour une des protéines virales structurales S, M, E ou N ou pour une protéine auxiliaire 3a, 3b, 6, 7a, 7b, 8, 9b.
Le processus de synthèse d’ARN viral subgénomique à partir d’ARN brin négatif est appelé transcription. Il correspond chez les eucaryotes à la synthèse d’ARNm à partir d’un brin d’ADN. L’ARN brin négatif sert donc à la fois de matrice pour la réplication et la transcription. Dans la transcription, seule la séquence du génome codant pour une enzyme est transcrite. A ce stade on est à plusieurs molécules différentes d’ARNm du virus, ce qui correspond aux divers ARN messagers des eucaryotes.
Les ARN subgénomiques sont ensuite traduits par la machinerie de traduction de la cellule parasitée et les protéines virales synthétisées via des organites cellulaires (réticulum endoplasmique et appareil de Golgi) sont finalement assemblées avec le génome viral ce qui conduit à la production de nouveaux virions. Ceux-ci sont libérés hors de la cellule par exocytose.
Conclusion
Le premier intérêt de cette étude est de faire une approche scientifique de ce qu’est un virus, de comprendre pourquoi sa reproduction est totalement dépendante de la cellule qu’il parasite pour la traduction en protéines de son génome. Mais cette exploitation de la cellule est dictée par les caractéristiques du génome viral. La reproduction du virus comprend comme chez les cellules eucaryotes, la réplication de son génome et son expression. Et ces processus bien que spécifiques au virus, mettent en évidence l’importance de la notion de complémentarité dans leur réalisation comme chez les eucaryotes. Enfin, le fait que l’ARNm du virus est traduit en protéine suivant le même code génétique que celui utilisé par la cellule pour ses propres protéines, aide à saisir que le monde viral, bien qu’inerte en dehors des cellules, s’intègre bien dans l’histoire du vivant.
Le deuxième intérêt de cette étude est de faire saisir que la connaissance des acteurs moléculaires du cycle viral peut déboucher sur la mise au point de médicaments susceptibles d’empêcher l’infection. Ainsi quatre protéines : la protéine S (Spike) qui conditionne l’entrée du virus dans une cellule, les protéines 3CLpro et PLpro qui, en clivant la polyprotéine permettent l’individualisation du complexe protéique indispensable à la réplication virale, la protéine RdRp (ARN polymérase ARN dépendante), enzyme clé de cette réplication, sont des cibles contre lesquelles les chercheurs essaient de mettre au point des molécules inhibitrices de leur action.


